EM菌に含まれる微生物の解析ー細菌類ーその2
前回、EM菌(EM1活性液)に含まれる細菌の構成を、メタ16S解析(V3V4領域)をした結果を報告しました。
この解析には一般的に行われている手法を用いましたが、その改良版が出されましたので、それを用いて再解析をしてみました。

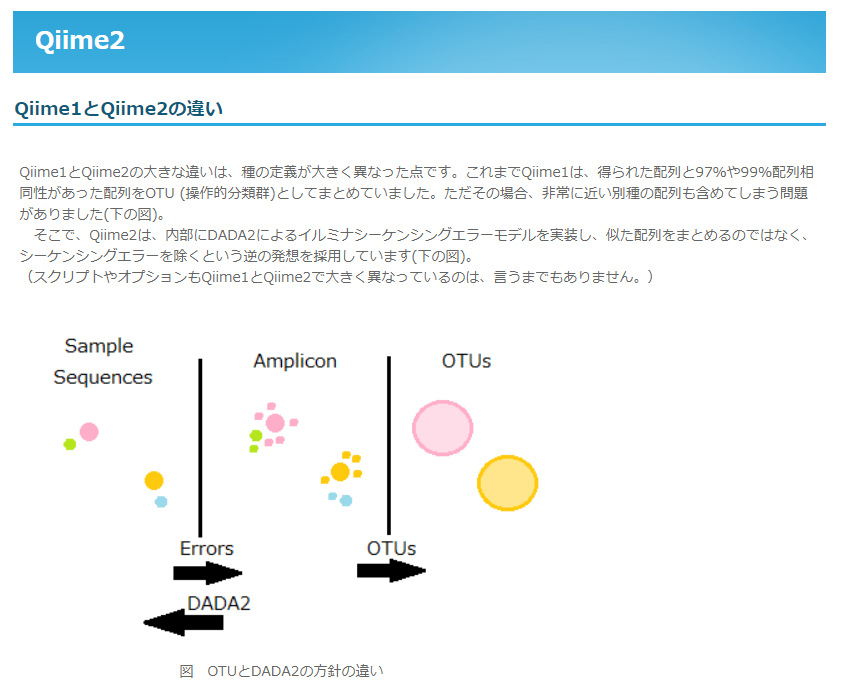
【QIIMEとQIIME2の違い】
解析パイプライン「QIIME」を改良した「QIIME2」の特徴として、NGS解析で得られたDNA配列データを分類する際のエラーを減らす「DADA2」という手法が取り入れられています。
・半田佳宏氏による解説
http://crusade1096.web.fc2.com/qiime2_renew.html
(参考文献)
前回のNGS解析によって得られたアンプリコンシーケンスデータ(fastqファイル)をQIIME2と精度が高いデータベースを組み合わせて再解析した結果を以下に示します。
【解析結果】

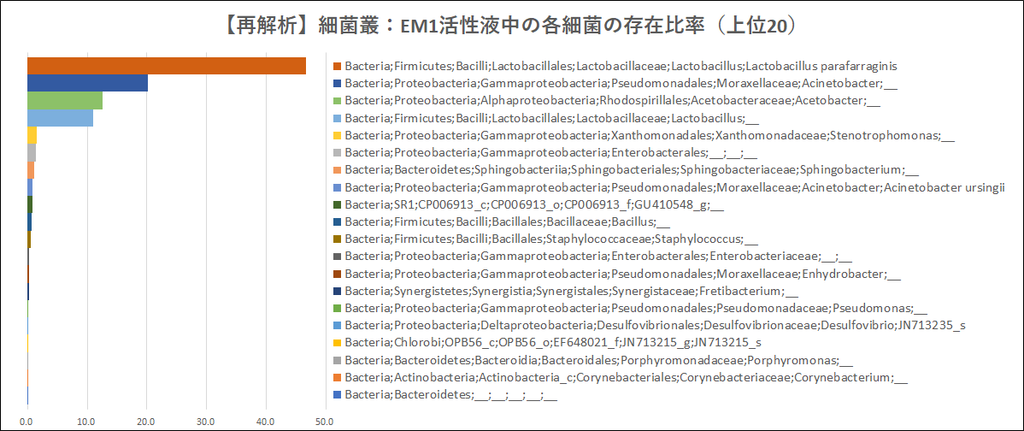

【EM1活性液中の細菌リスト】上位10
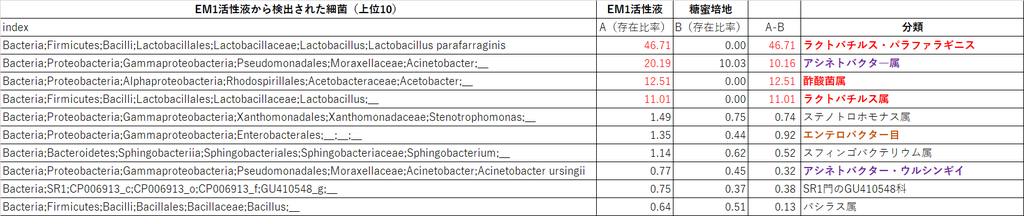
(↑クリックで拡大)
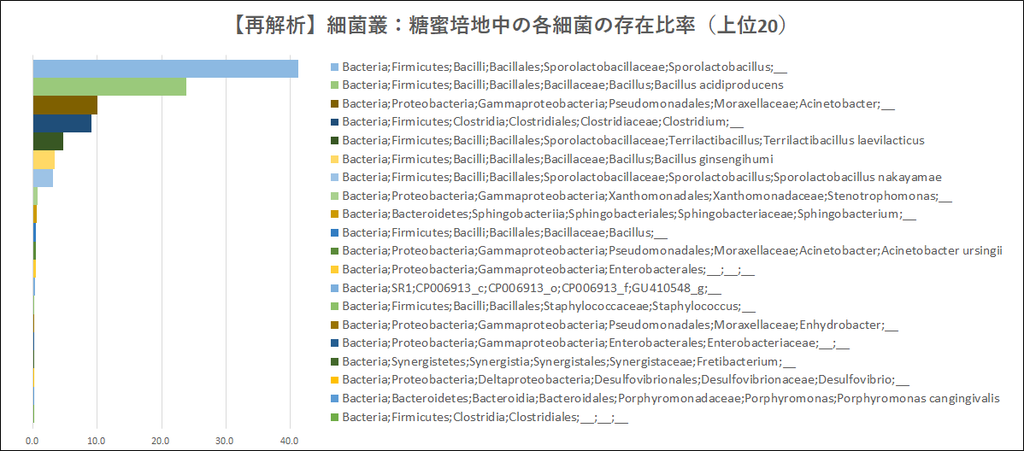
【糖蜜培地中の細菌リスト】(上位10)
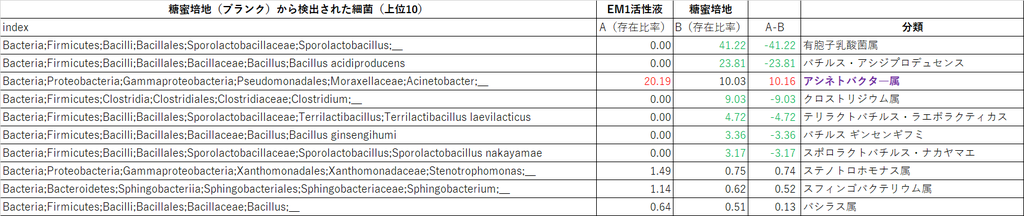
(↑クリックで拡大)

【EM1活性液で増えた細菌リスト】上位10
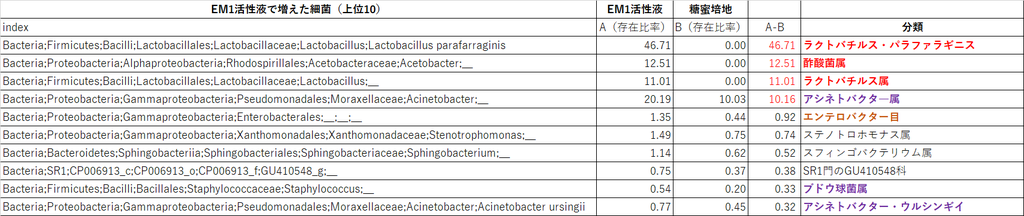
(↑クリックで拡大)

【EM1活性液で減った細菌リスト】上位10
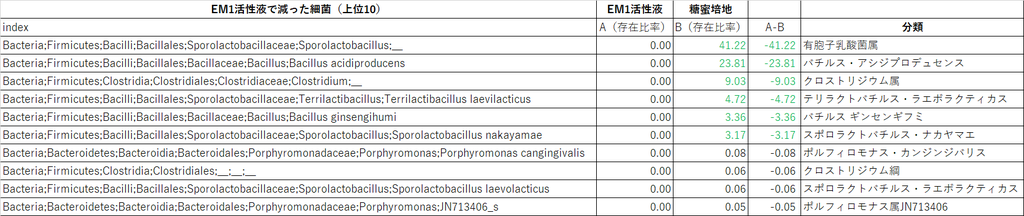
(↑クリックで拡大)
【解析費用】